国内首个二代基因测序FPGA加速方案-背后的技术
二代基因组测序NGS(Next Generation Sequencing下一代基因组测序)是一种新型基因检测技术,它可以从血液或者唾液中分析测定基因全序列,用来预测疾病,个人的行为特征等等。随着测序成本不断降低并逼近数据分析成本,同时随着近年基因数据量爆发式增长,数据分析成为瓶颈,而传统方法计算速度慢,效率低,因此高性能计算势在必行。
如下图1所示,二代全基因组分析流程一般可以分为5步。
第一步,Decompression。无损解压还原原始样本。因为基因样本数据量极大,所以对存储和传输带来困难。为了节省传输带宽和成本,一般会对FASTQ文件进行压缩后再进行本地存储和网络传输。
第二步,Alignment。建立参考基因组索引,然后对比短序列和参考基因组, 目的是为了确定短序列在基因组上的位置。
第三步,Sorting。把短序列调整成按照染色体分类进行排列。
第四步,Mark duplicate。标记和去除其中重复的序列。
第五步,Variant Calling。寻找样本数据和参考基因组数据的差异,列举出所有的差异点。通过检测变异最终生成一个vcf/gvcf文件,该文件中会包含所有样本的变异位点和基因型信息。
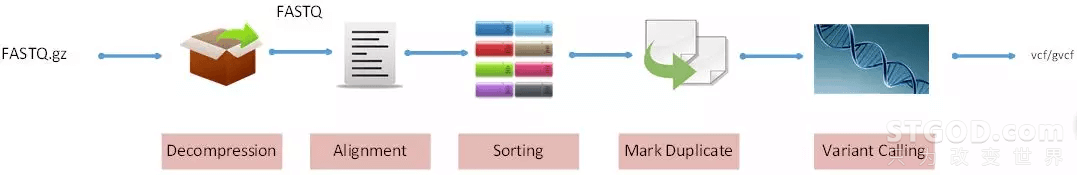
图1:基因二代NGS计算流程
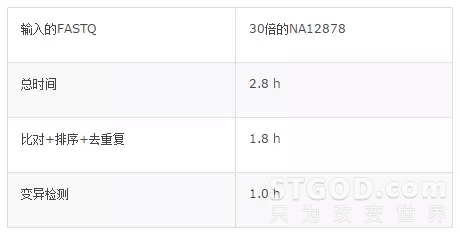
针对二代全基因组分析流程计算时间长,效率不高等问题,腾讯云基因团队近日推出了基于腾讯极光异构系统(Tencent Aurora Heterogeneous System)的二代NGS加速方案,可将人类全基因组分析从30小时优化到2.8小时,加速比超过10倍。在实验过程中,研究人员采用一份30倍测序深度的人类全基因组FASTQ文件(NA12878),分别在一台业界常用的通用高性能服务器和一台搭载腾讯极光异构系统的服务器上进行测试。通用高性能服务上的分析运行了30个小时,而使用极光技术的解决方案在没有对流程和算法进行删减的条件下,只需2.8小时便完成从FASTQ到vcf的整个处理流程。
表1:二代全基因组分析耗时
 如下图2,3所示,传统的计算系统一般采用多个高端CPU搭建HPC系统以缩短计算时间,时间缩短的同时成本往往会增加,这不利于业务的大规模扩展。腾讯极光异构系统在提供卓越性能的同时,还能进一步降低客户的成本。它采用自研核心技术极光(Aurora Technology),通过三个方面整体优化传统的分析和计算流程。
如下图2,3所示,传统的计算系统一般采用多个高端CPU搭建HPC系统以缩短计算时间,时间缩短的同时成本往往会增加,这不利于业务的大规模扩展。腾讯极光异构系统在提供卓越性能的同时,还能进一步降低客户的成本。它采用自研核心技术极光(Aurora Technology),通过三个方面整体优化传统的分析和计算流程。第一,搭载BWA_MEM和Variant Calling专用硬件算法核。采用业界顶尖的大规模集成电路设计技术,把算法性能提升了一个台阶。
第二,算法级优化内存访问的方式。
第三,IO瓶颈导致系统性能无法提升一直是基因二代分析流程的一大痛点,通过系统和算法级别优化以及异构加速大幅降低IO带宽需求。
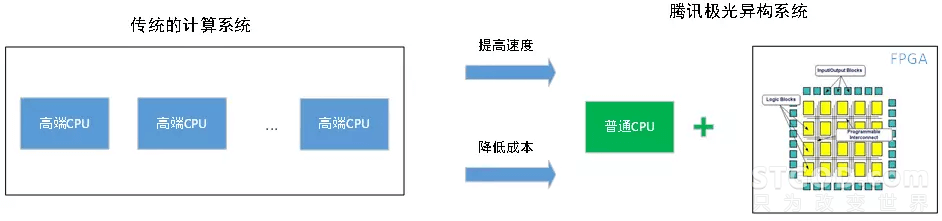 图2:腾讯极光异构系统
图2:腾讯极光异构系统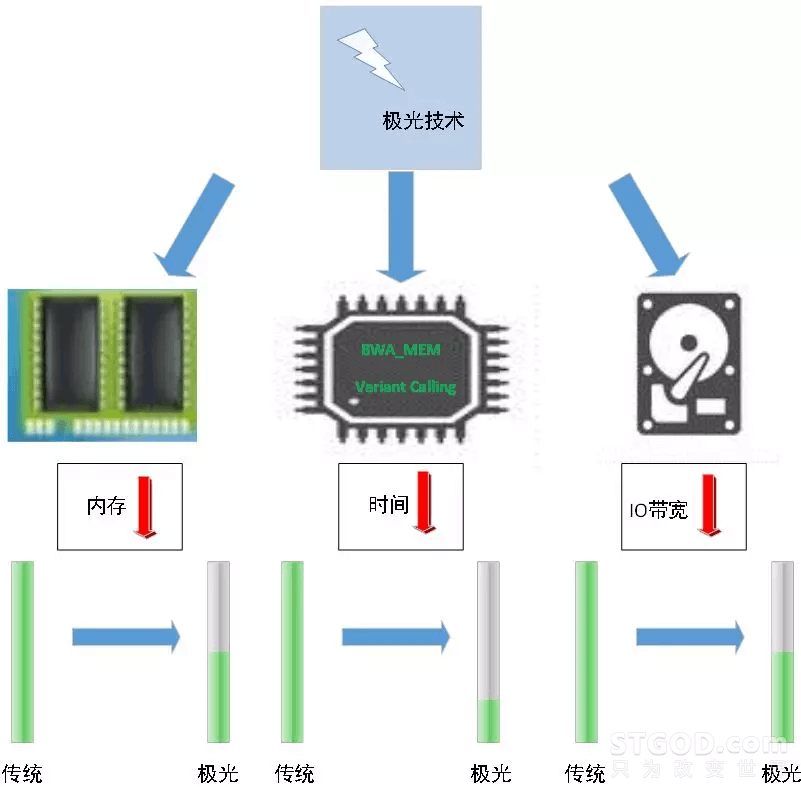 图3:腾讯极光技术
图3:腾讯极光技术接下来将对极光的三大核心技术进行介绍,分别对应是极光架构(Aurora Genomic Architecture),极光流水线(Aurora Genomic Pipeline),极光并行计算技术(Aurora Genomic Parallel Computing)。
1、一般高端CPU包含有限个物理核,而极光架构里面有上千个以上针对基因应用的专用算法核。
2、极光流水线技术通过对复杂任务的合理拆分提升整体系统的吞吐。
3、极光并行计算技术把传统的串行计算通过算法调整转换为多个数据流的并行运算。
 图4:腾讯极光基因架构
图4:腾讯极光基因架构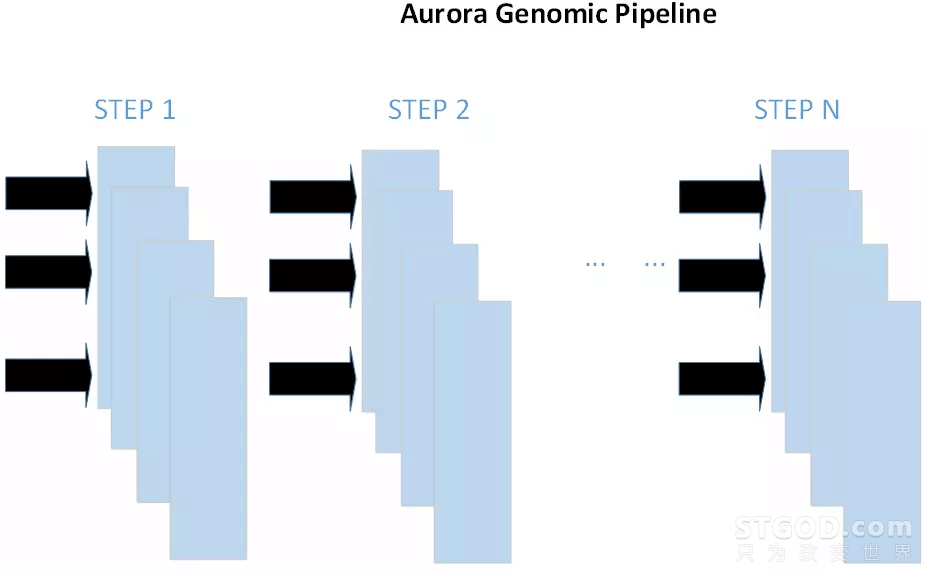
图5:腾讯极光流水线技术(Aurora Genomic Pipeline)
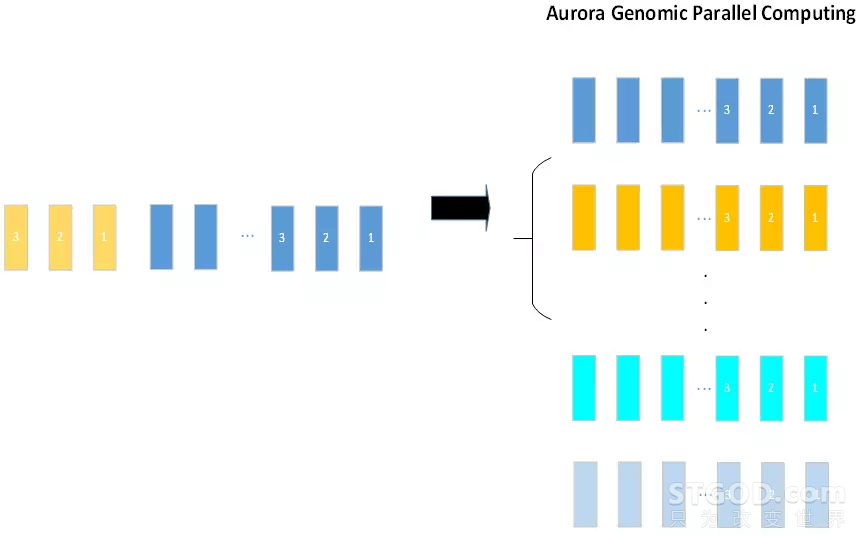 图6:腾讯极光并行计算技术
图6:腾讯极光并行计算技术在极大提升分析效率的同时,腾讯极光异构系统还保证了优异的分析准确率,与传统软件分析准确率基本一致。研究人员将通用服务器上和极光芯片服务器计算得出的分析结果,上传PrecisionFDA网站进行比对。比对结果如下图7和图8所示:
 图7:通用处理器方案测试结果
图7:通用处理器方案测试结果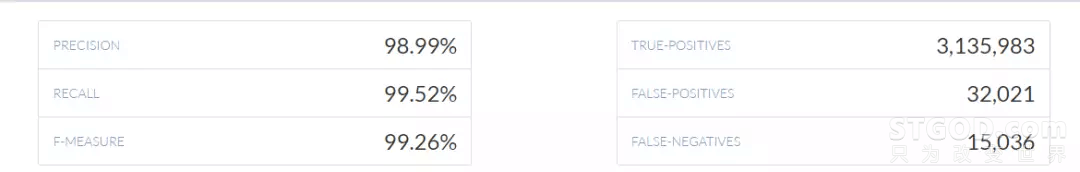 图8:极光异构系统测试结果
图8:极光异构系统测试结果作者:STGOD
转载请标明出处:https://stgod.com/3924/